En los últimos años, se ha hablado mucho de la "microbiota" de los cerdos. Muchos estudios científicos han analizado la microbiota y su impacto en la producción y la salud, pero no tenemos una imagen clara de cómo es una "microbiota saludable". ¿Qué es la microbiota y cómo puede ayudar a mantener la salud de los cerdos? Te lo explicamos.
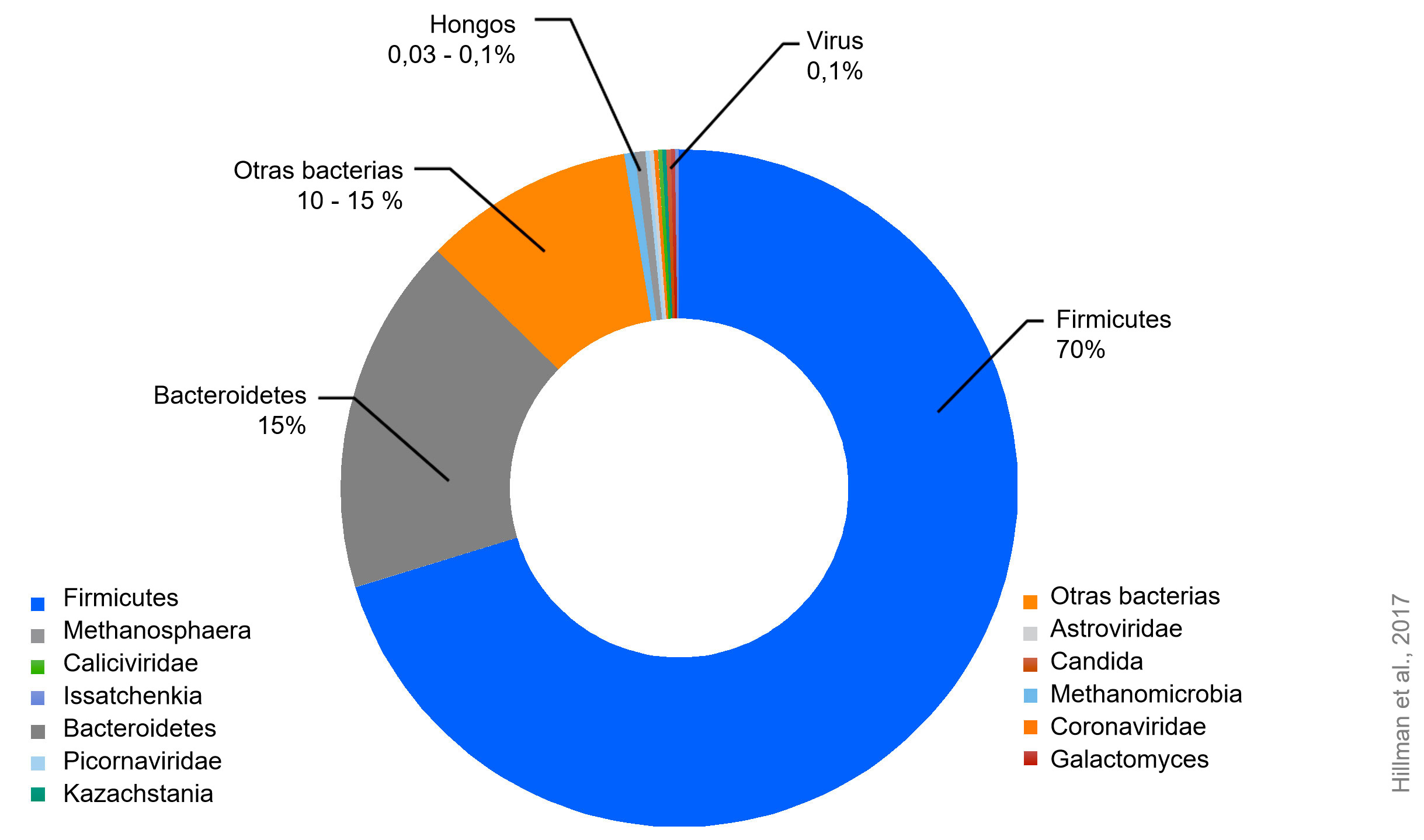
Microbiota es una palabra acuñada a partir del término ecológico biota, que significa cualquier tipo de forma de vida que se encuentra en una región o hábitat determinado. La microbiota, por tanto, se refiere a la biota microscópica, es decir, a todos los microorganismos que se encuentran en un lugar determinado (por ejemplo, la composición de la microbiota del intestino porcino que se muestra en la figura 1). Este término incluye la bacteriota (cuando se habla sólo de bacterias), la virota (sólo de virus) o la micobiota (sólo de hongos). No debe confundirse con el microbioma (u otros términos que terminan en "-oma"), que significa la colección de genomas en una muestra determinada. Los genomas son el conjunto de genes de un organismo determinado. La microbiota y el microbioma no son lo mismo, pero a menudo se utilizan indistintamente.


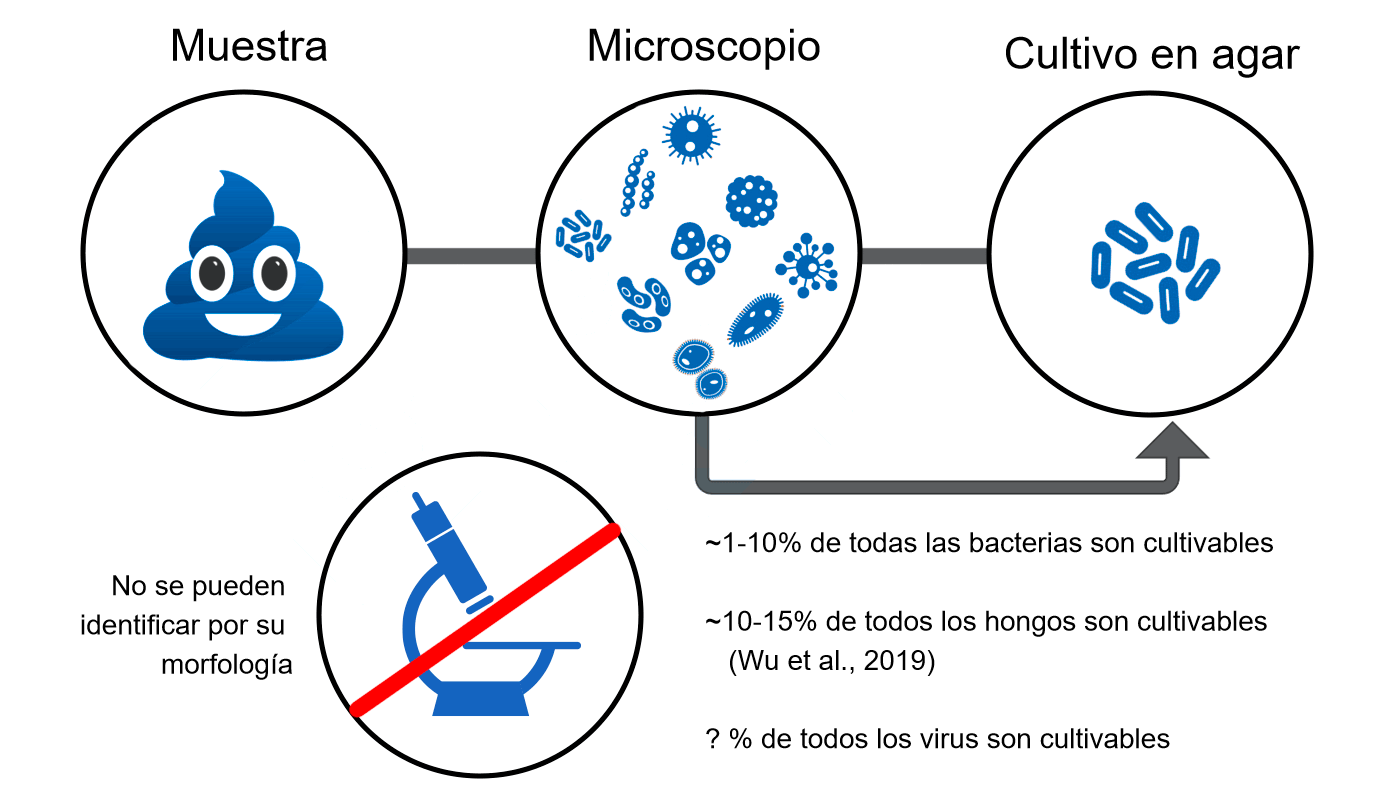
El estudio de microbiotas es extremadamente complejo y desafiante. De hecho, la mayoría de los estudios sobre "microbiota" están mirando otra cosa. A diferencia de un biólogo que utiliza prismáticos para observar guacamayos salvajes en la selva brasileña, los microbiólogos no pueden limitarse a mirar los virus y verlos interactuar. De hecho, no podemos cultivar muchos de los microorganismos en el laboratorio utilizando protocolos rutinarios (Kogure et al., 1979; Staley y Konopka, 1985). Este problema es de tal magnitud que los científicos lo denominaron "la gran anomalía del recuento en placa", un fenómeno en el que, pese a observar una gran diversidad de microorganismos al microscopio, el cultivo en el laboratorio no la refleja (figura 2). Esto se explica por nuestro limitado conocimiento de los requisitos nutricionales y ambientales de cada microorganismo, probablemente sólo conocemos una proporción muy limitada de todos los microbios. Entonces, ¿cómo se estudia la microbiota?
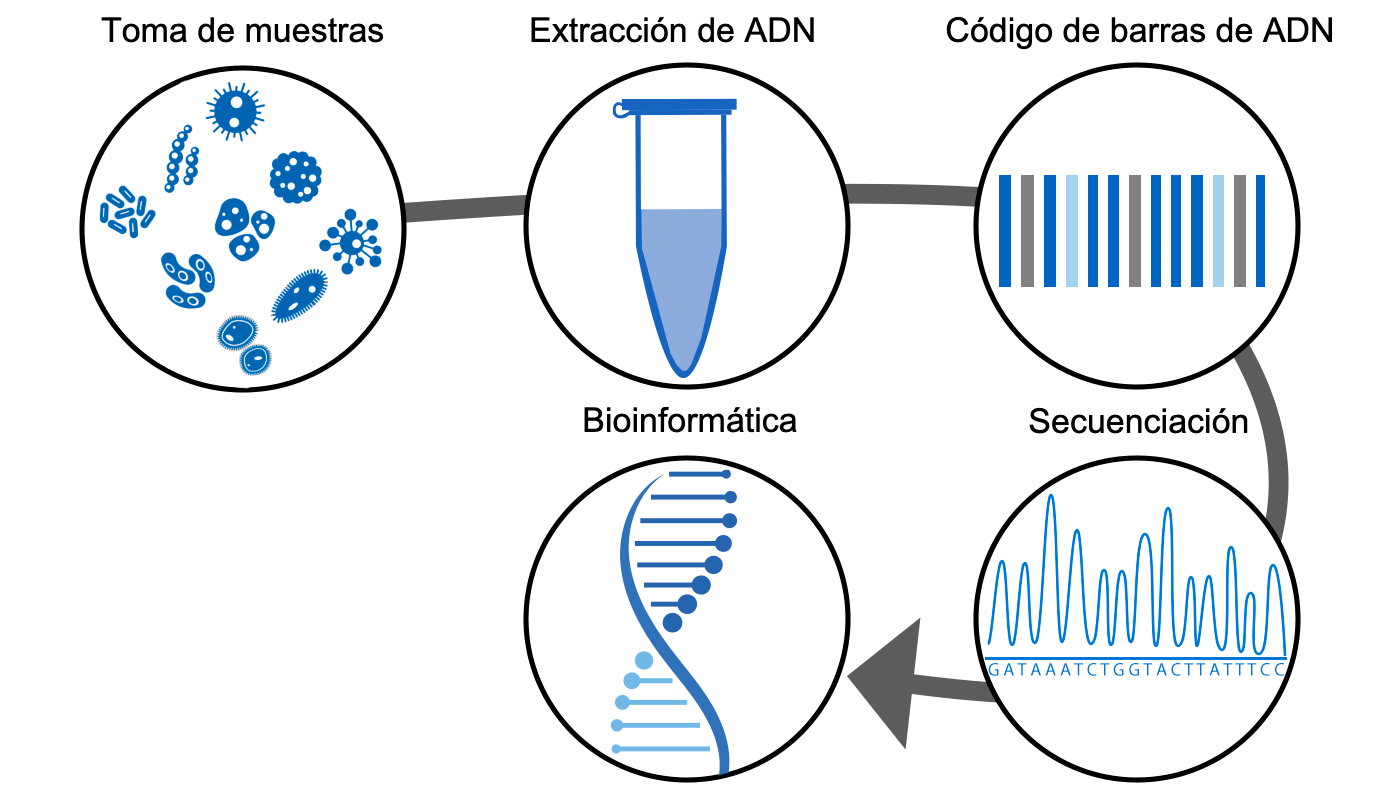
La respuesta es la secuenciación. Secuenciamos sus genomas y utilizamos su secuencia de ADN para identificarlos y comprender cómo interactúan entre sí y con sus huéspedes porcinos. La secuencia de ADN de cada microbio (y de cualquier otro ser vivo) funciona como un código de barras. Al "escanear" este código de barras, podemos identificar el "producto" (el microbio). Por lo tanto, la gran mayoría de lo que sabemos sobre la microbiota proviene del conocimiento del microbioma. Pero, ¿por qué no podemos domesticar la microbiota como hicimos con los perros hace 10.000 años, y hacerla trabajar para nosotros?
La mayor parte de la investigación, hasta ahora, se ha centrado en responder a la pregunta de "¿Quién está ahí?" en el microbioma. Aunque este es un paso importante, ahora se está reconociendo que, más importante que saber "¿Quién?", es saber "¿Qué hace?". Además. hay algunas salvedades cuando se trata de las tecnologías de secuenciación del ADN y de traducir esta gran cantidad de datos en soluciones útiles:
- El ADN está presente en todas partes. Esto significa que hay contaminación en casi todos los pasos del análisis (Salter et al., 2014). Esto puede distorsionar los datos y los resultados, a menos que haya controles muy estrictos, y a menudo no los hay.
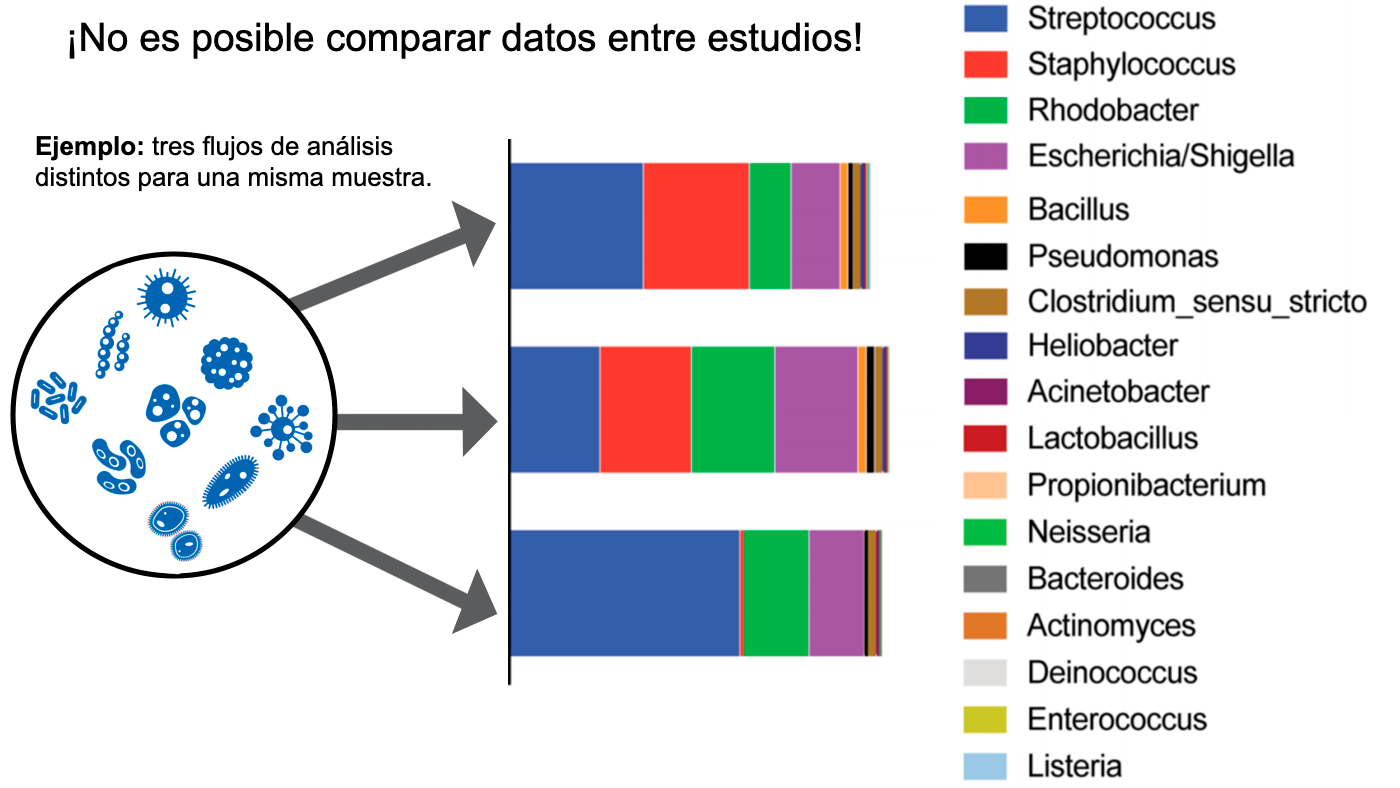
- Las herramientas utilizadas para analizar los datos del microbioma no están estandarizadas, y cada una de ellas tiene un sesgo importante. Esto significa que es muy difícil comparar los datos de un estudio con otro.
- Hay MUCHOS microbios (sólo en el colon hay 1014). Todos son diferentes, y tenemos muy poca información sobre la mayoría de ellos y sobre qué pueden hacer y cómo lo hacen.
- Cualquier actividad significativa suele provenir de microbios raros, lo que significa que estamos buscando una aguja en un pajar sin saber cómo es la aguja.
- Hay interacciones entre los microbios que no entendemos/conocemos, así que ¿cómo podemos buscarlas?
- La microbiota es compleja y MUY variable. Varía entre huéspedes (cerdo vs vaca), entre sitios (ojo de cerdo vs boca de cerdo), entre momentos del día (mañana vs noche, Liang y FitzGerald, 2017; Voigt et al., 2016). Esencialmente, cada vez que lo miramos vemos algo diferente.
Existe la percepción de que algunos de estos retos se abordarán en los próximos años a medida que las tecnologías de secuenciación de ADN sean más eficientes y accesibles, y se desarrolle una mejor detección de contaminantes. En nuestro próximo artículo de esta serie, veremos cómo se interpretan los datos del microbioma, lo que sabemos hasta ahora sobre el microbioma porcino y cómo se está avanzando para aprovechar su potencial para mejorar la salud y la producción.