Секвенирование и интерпретация его результатов при использовании в программах борьбы с РРСС
21-Сен-2015 (назад 10 года 8 месяцы 4 дни)
Вступление
Геном вируса репродуктивно-респираторного синдрома свиней (РРССВ) представлен одноцепочечной молекулой РНК, что объясняет его крайнюю подверженность генетическим мутациям. Это также делает каждый штамм вируса РРСС уникальным - настолько, что генотипирование является весьма полезным методом диагностики и борьбы с заболеванием. Диагностическое генотипирование проводится путем определения последовательности нуклеотидов на отрезке ДНК, копирующем геномный фрагмент вирусной РНК (секвенирование ДНК). Наиболее часто для этого в настоящее время используется фрагмент ORF5 – ген, кодирующий основной оболочечный гликопротеин. В значительной мере это обусловлено тем, что он обладает неограниченным генетическим разнообразием.
Диагностическое секвенирование ДНК
Разница между вирусами РРСС первого (европейский) и второго (американский) типа легко выявляется с помощью большинства диагностических ПЦР-тест-систем. В то же время, установление различий между отдельными штаммами каждого из этих двух генотипов требует проведения секвенирования ДНК. С этой целью биологические жидкости или ткани, содержащие вирус РРСС в умеренных или высоких концентрациях, обрабатываются таким образом, чтобы изолировать РНК, которая затем копируется на ДНК методом обратной транскрипции, после чего ген ORF5 амплифицируется с помощью ПЦР и попадает на оборудование для проведения секвенирования ДНК. Этот процесс почти полностью автоматизирован и обычно занимает от одного до трех дней. Полученные в результате необработанные данные поступают в диагностическую лабораторию для анализа. Стандартный отчет о результатах содержит описание нуклеотидных последовательностей исследованного штамма, его сходство со стандартными штаммами, используемыми в вакцинах. Некоторые лаборатории, помимо этого, предоставляют результаты сравнения со стандартными панелями изолятов вируса РРСС дикого типа, представленные в виде дендрограмм. Также, могут предоставляться данные о результатах сравнения с последовательностями РРССВ, описания которых содержатся в производственной базе данных.
Анализ последовательностей РРССВ
Схожесть или идентичность последовательностей выявляется путем сопоставления двух или более последовательностей с помощью компьютерной программы. Пример сопоставления нескольких последовательностей ORF5 с пяти различных ферм приведен на Рис.1. Попарные сравнения процентной степени их идентичности, лежащие в пределах от 81,2% до 99,8%, представлены в таблице. Дендрограмма результатов полигенетического анализа демонстрирует группировку схожих последовательностей (Рис.2). Ключевой вопрос, встающий перед производителями и ветеринарами, это – являются ли выявленные генетические различия в последовательностях обычными вариациями одного и того же штамма вируса РРСС или они свидетельствуют о присутствии на ферме различных штаммов?

Рис.1. Фрагмент сопоставления последовательностей ORF5 штаммов вируса РРСС пяти разных ферм. С ферм 1, 4 и 5 было получено по нескольку последовательностей. Точки в последовательностях соответствуют позициям, идентичным референтному штамму Lelystad вируса РРСС первого типа.
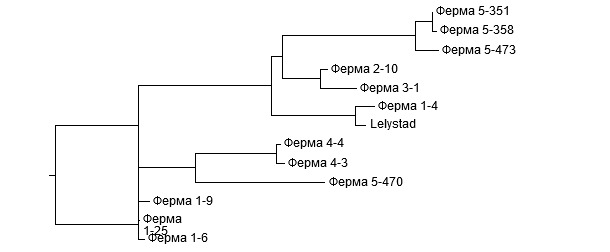
Рис.2. Дендрограмма последовательностей ORF5, полученных для пяти разных ферм. Пример расшифровки: на Ферме 1 присутствуют 2 несвязанных штамма. Степень идентичности трех последовательностей друг другу >99%, в то время, как четвертая соответствует им только на ~83%. Зато она соответствует вирусу Lelystad. Два штамма с Фермы 4 тесно связаны друг с другом (идентичны на 99,5%). На Ферме 5 присутствуют два несвязанных штамма. Степень соответствия трех штаммов друг другу >98%, а четвертому – только около 81%.
Таблица. Попарное представление идентичности всех сопоставленных последовательностей ORF5 серий образцов вируса РРСС первого типа в процентах.
| 1-4 | 1-6 | 1-9 | 1-25 | 2-10 | 3-1 | 4-4 | 4-3 | 5-351 | 5-358 | 5-470 | 5-473 | Lelystad | |
| *** | 83.5 | 83.3 | 83.7 | 93.2 | 92.6 | 86.1 | 86.0 | 88.1 | 88.0 | 83.2 | 88.3 | 98.7 | 1-4 |
| *** | 99.2 | 99.7 | 84.2 | 83.0 | 86.0 | 86.0 | 81.4 | 81.2 | 86.3 | 81.4 | 82.1 | 1-6 | |
| *** | 99.5 | 84.5 | 83.3 | 85.6 | 85.6 | 81.4 | 81.2 | 86.5 | 81.4 | 81.9 | 1-9 | ||
| *** | 84.5 | 83.3 | 86.0 | 86.0 | 81.7 | 81.5 | 86.8 | 81.7 | 82.2 | 1-25 | |||
| *** | 98.2 | 86.6 | 86.5 | 91.1 | 90.9 | 84.2 | 90.4 | 93.3 | 2-10 | ||||
| *** | 84.4 | 84.2 | 90.2 | 90.0 | 83.3 | 89.7 | 92.9 | 3-1 | |||||
| *** | 99.5 | 82.5 | 82.7 | 90.6 | 82.5 | 84.8 | 4-4 | ||||||
| *** | 82.3 | 82.5 | 90.9 | 82.2 | 84.6 | 4-3 | |||||||
| *** | 99.8 | 81.0 | 98.3 | 88.4 | 5-351 | ||||||||
| *** | 81.2 | 98.2 | 88.2 | 5-358 | |||||||||
| *** | 80.9 | 83.2 | 5-470 | ||||||||||
| *** | 88.8 | 5-473 | |||||||||||
| *** | Lelystad |
Интерпретация последовательностей РРССВ
Последовательность ORF5 содержит около 600 нуклеотидов. Общая мутируемость этого гена, по разным оценкам, составляет от 0,5% до 1% в год. Отличия в скорости генетических изменений определяются различными факторами невирусной природы. На репликацию и трансмиссивность вируса РРСС у свиней большое внимание оказывает уровень их специфического и неспецифического иммунитета, создающий сильное ингибирующее давление, приводящее к уменьшению числа вирусных копий. Уменьшение вирусной нагрузки приводит к снижению трансмиссивности, снижая тем самым общую репликацию вируса и степень его изменчивости. Таким образом, иногда может наблюдаться более высокая или более низкая генетическая изменчивость, выходящая за предполагаемые рамки 0,5%-1% в год.
Главным вопросом при проведении генетического анализа является вопрос о том, являются ли две последовательности близкородственными (двумя вариантами одного и того же штамма) или независимыми (принадлежащим двум несвязанным штаммам). Общепринято, что вывод о том, связаны ли изоляты вируса РРСС или нет, делается, исходя из степени схожести, попадающей в интервал достоверности 97% или 98%. Очевидно, что безоговорочное, сделанное без учета всех сопутствующих факторов, принятие за основу предпосылки о двух- или трехпроцентной генетической разнице между двумя изолятами может привести к неверным выводам. Различия между двумя вариантами одного и того же штамма, циркулирующего в поголовье на протяжении нескольких лет, постепенно выбьются за пределы данного интервала. Степень достоверности выводов о близкородственности может быть повышена получением доступа к дополнительной информации, включая даты и локализацию получения изолятов. Очень важен анализ, противопоставляющий новые последовательности РРССВ широкому референтному набору, являющемуся показательным для фермы, региона, используемой технологии или даже генетического разнообразия в глобальном масштабе.
Секвенирование ДНК штаммов вируса РРСС может вскрыть их родственность или независимость (Рис.2), но не может быть использовано для прогноза или объяснения степени иммунологической защиты или вспышек в иммунных поголовьях. Также, секвенирование ДНК не позволяет судить о клинических последствиях инфицирования данным конкретным штаммом, в силу того, что идентификация генетических маркеров вирулентности отсутствует.
В настоящее время, в основном в США, но также и в Европе осуществляется множество региональных проектов по борьбе с РРСС. Полное представление о том, с какими разновидностями вируса приходится иметь дело при начале мероприятий по обузданию инфекции и борьбе с ней является критичным как для эффективного их мониторинга, так и для идентификации новых, интродуцированных на фермах или в регионе, штаммов.
